Ⅰ. Aumentà a sensibilità di u sistema di reazione:
1. Separate RNA d'alta qualità:
A sintesi di cDNA successu vene da RNA di alta qualità.L'RNA di alta qualità deve assicurà almenu un totale più longu è ùn cuntene micca inhibitori chì ùn cuntenenu micca enzimi di registrazione, cum'è EDTA o SDS.A qualità di RNA determina u valore massimu di l'infurmazioni di sequenza chì pudete trascrive à u cDNA.U metudu generale di purificazione di l'RNA hè un metudu passu per aduprà isoocianate / acidofenol.Per prevene a contaminazione di RNase, l'RNA siparatu da una mostra ricca in RNase (cum'è u pancreas) richiede u almacenamentu di formaldeide per salvà RNA d'alta qualità, chì hè ancu più cusì per u almacenamiento à longu andà.L'RNA estratto da u fegato di u ratu hè statu degradatu basicamente dopu una settimana di almacenamiento in acqua, mentre chì l'RNA estratto da u spleen di u ratu hè statu stabile dopu à trè anni di almacenamiento in acqua.Inoltre, e trascrizioni più grande di 4kb sò più sensibili à a degradazione di a traccia di RNasi cà e trascrizioni chjuche.Per aumentà a stabilità di a mostra di RNA di almacenamiento, l'RNA pò esse dissolutu in una methalmamine di ioni, è hè almacenatu -70 ° C.Thylide utilizatu per salvà l'RNA ùn deve micca cuntene un oggettu miscellaneo chì degrada l'RNA.L'RNA, chì hè derivatu da u pancreas, pò esse salvatu in methalmamine per almenu un annu.Quandu site prontu à aduprà RNA, pudete aduprà i seguenti metudi per precipitate RNA: aghjunghje NaCl à 0,2 m è 4 volte u voluminu di etanol, mette a temperatura di l'ambienti per 3-5 minuti, è 10 000 × g centrifuga per 5 minuti.
2. Aduprate transcriptase inversa senza attività RNaseH (RNaseH-):
L'inhibitori di RNase sò spessu aghjuntu à e reazzioni di trascrizione inversa per aumentà a durata è u rendiment di a sintesi di cDNA.L'inhibitore di RNase hè aghjuntu in a prima reazione di sintesi di a catena in presenza di buffers è agenti riducenti cum'è DTT perchè u prucessu di sintesi pre-cDNA denatura l'inhibitore, liberando cusì RNases ligati chì degradanu l'RNA.L'inhibitore di a proteina RNase impedisce solu a degradazione di l'RNA da RNase A, B, C, è ùn impediscenu micca RNases nantu à a pelle, cusì deve esse cura di ùn introduci RNases da i dite malgradu l'usu di sti inhibitori.
A transcriptase inversa catalizza a cunversione di RNA in cDNA.Sia M-MLV è AMV anu attività RNaseH endogena in più di a so propria attività di polimerasi.L'attività RNaseH compete con l'attività polimerasi per i filamenti eterozigoti formati tra i modelli di RNA e i primers di DNA o i filamenti di estensione cDNA, e degrada RNA: filamenti di RNA in complessi di DNA.I mudelli di RNA degradati da l'attività RNaseH ùn ponu più esse aduprati cum'è sustrati efficaci per a sintesi di cDNA, riducendu u rendiment è a durata di a sintesi di cDNA.Cusì l'eliminazione o a riduzzione di l'attività RNaseH di a transcriptase inversa seria di grande benefiziu.
SuperScriptⅡ reverse transcriptase, MMLV reverse transcriptase di RNaseH- è thermoScript reverse transcriptase, AMV di RNaseH- cedeu più cDNA full-length cà MMLV è AMV.A sensibilità RT-PCR hè affettata da a quantità di cDNA sintetizatu.ThermoScript hè assai più sensibile cà AMV.A dimensione di i prudutti RT-PCR hè limitata da l'abilità di a transcriptase inversa per sintetizà cDNA, soprattuttu quandu clone Cdna più grande.In cunfrontu cù MMLV, SuperScripⅡ hà aumentatu significativamente u rendiment di i prudutti RT-PCR longu.A transcriptase inversa di RNaseH- aumenta ancu a stabilità termale, cusì a reazione pò esse realizata à temperature più altu di u normale di 37-42 ℃.In e cundizioni di sintesi suggerite, i primers oligo(dT) è 10μCi α-p]dCTP sò stati utilizati.A pruduzzione tutale di a prima catena hè stata calculata cù u metudu di precipitazione TCA.L'ADNc di lunghezza tutale hè statu analizatu utilizendu a rimozione di strisce di taglia è cuntendu in un gel d'agarose alkaline.
3. Aumentà a temperatura di conservazione di u calore di a trascrizione inversa:
A temperatura di mantene più alta aiuta à apre a struttura secundaria di RNA è aumentà u rendiment di a reazione.Per a maiò parte di i mudelli di RNA, tenendu l'RNA è l'amorce à 65 ° C senza buffer o sali è poi rinfriscà rapidamente nantu à u ghjacciu elimina a maiò parte di e strutture secondarie è permette à i primers di ligà.Tuttavia, certi mudelli anu sempre una struttura secundaria, ancu dopu a denaturazione termale.L'amplificazione di sti mudelli difficiuli pò esse realizatu utilizendu a transcriptase inversa ThermoScript è mettendu a reazione di transcriptase inversa à temperature più alte per migliurà l'amplificazione.Temperature di mantene più elevate ponu ancu aumentà a specificità, soprattuttu quandu a sintesi di l'ADNc hè realizatu cù primers gene-specific primers (GSPS) (vede u Capitulu 3).Si l'on utilise GSP, assurez-vous que la valeur Tm de l'amorce soit la même que la température de maintien prévue.Ùn aduprate micca oligo (dT) è primers aleatoriu sopra à 60 ℃.I primers casuali sò tenuti à 25 ℃ per 10 minuti prima di aumentà à 60 ℃.In più di l'usu di temperature di trascrizione inversa più elevate, a specificità pò esse migliurata trasferendu direttamente a mistura di RNA / primer da a temperatura di denaturazione di 65 ℃ à a temperatura di mantene a trascrizione inversa è aghjunghjendu una mistura di reazione 2× preriscaldata (sintesi d'iniziazione termale cDNA).Stu approcciu aiuta à prevene l'accoppiamentu di basa intermolecular chì si trova à a temperatura più bassa.L'usu di un strumentu PCR simplificà i numerosi interruttori di temperatura necessarii per a RT-PCR.
Tth polimerasi stabilizzata da u calore agisce cum'è DNA polimerasi in presenza di Mg2+ è RNA polimerasi in presenza di Mn2+.Pò mantene u calore finu à 65 ℃.In ogni casu, a prisenza di Mn2 + durante a PCR riduce a fideltà, chì rende a polimerasi Tth menu adattata per l'amplificazione d'alta precisione, cum'è a clonazione di cDNA.Inoltre, Tth hè menu efficiente à a trascrizione inversa, chì riduce a sensibilità, è postu chì una sola enzima pò esse realizatu a trascrizione inversa è a PCR, e reazzioni di cuntrollu senza trascrizzione inversa ùn ponu esse usate per distingue i prudutti amplificati di cDNA da quelli di DNA genomicu contaminatu.
4. Additivu chì prumove a trascrizione inversa:
L'aghjunzione di additivi, cumpresa a glicerina è DMSO, à a prima reazzione di sintesi di a catena pò riduce l'stabilità di a doppia fila di l'acidu nucleicu è unwind a struttura secundaria di RNA.Finu à 20% glicerina o 10% DMSO pò esse aghjuntu senza affettà l'attività di SuperScriptⅡ o MMLV.L'AMV pò ancu tollerà finu à u 20% di glicerol senza riduce l'attività.Per maximizà a sensibilità di RT-PCR in a reazione di trascrizione inversa SuperScriptⅡ, 10% di glicerol pò esse aghjuntu è insulatu à 45 ℃.Se 1/10 di u pruduttu di retrotranscription-reaction hè aghjuntu à a PCR, a cuncentrazione di glicerol in a reazione di amplificazione hè di 0,4%, chì ùn hè micca abbastanza per inibisce a PCR.
5. Trattamentu RNaseH:
A sensibilità pò esse migliurata da u trattamentu di reazzioni di sintesi di cDNA cù RNaseH prima di a PCR.Per certi mudelli, hè pensatu chì l'RNA in a reazione di sintesi di cDNA impedisce a ligame di i prudutti amplificati, in quale casu u trattamentu RNaseH pò aumentà a sensibilità.In generale, u trattamentu RNaseH hè necessariu per l'amplificazione di un mudellu di destinazione cDNA di lunghezza relativamente longa, cum'è scherosi tuberosaⅡ cù copia bassa.Per questu mudellu difficiule, RNaseH hà rinfurzatu u signale generatu da u cDNA sintetizatu da SuperScriptⅡ o AMV.Per a maiò parte di e reazioni RT-PCR, u trattamentu RNaseH hè facoltativu perchè u passu di denaturazione PCR isolata à 95 ℃ tipicamente idrolizza l'RNA da u cumplessu RNA: DNA.
6. Metudi migliurati per a rilevazione di picculi quantità di RNA:
RT-PCR hè particularmente sfida quandu solu picculi quantità di RNA sò dispunibili.L'aghjunzione di glucogenu cum'è un traspurtadore durante a separazione di RNA aiuta à aumentà u rendiment di picculi campioni.Un glucogenu senza RNase pò esse aghjuntu à u stessu tempu cù Trizol.U glucogenu hè soluble in acqua è pò stà in a fase di l'acqua cù RNA per aiutà à a precipitazione sussegwenti.A cuncentrazione cunsigliata di glucogenu senza RNasi hè 250μg/ml per campioni menu di 50mg di tissutu o 106 cellule cultivate.
L'aghjunzione di BSA acetilata à e reazzioni di trascrizzione inversa cù SuperScriptⅡ pò aumentà a sensibilità, è per picculi quantità di RNA, riducendu a quantità di SuperScriptⅡ è aghjunghjendu 40 unità di RnaseOut nuclease inhibitor pò migliurà u livellu di rilevazione.Se u glicogenu hè utilizatu in a separazione di l'RNA, l'aghjunzione di l'inibitori di BSA o RNase per reverse reazioni di trascrizzione cù SuperScriptⅡ hè sempre cunsigliatu.
Ⅱ. Aumentà a specificità di RT-PCR
1. Sintesi cNDA:
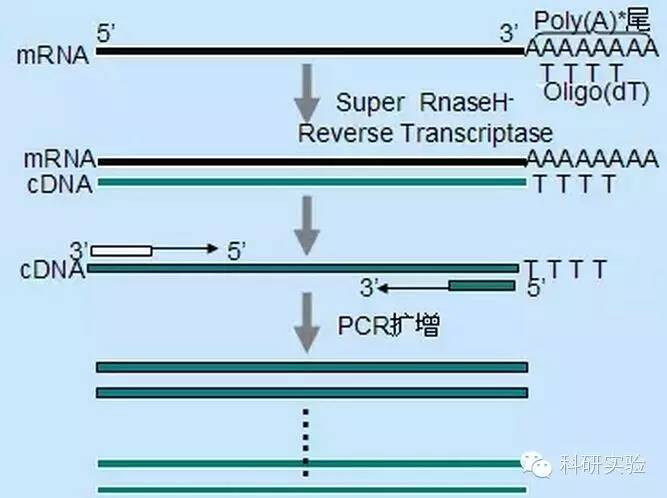
Trè metudi diffirenti ponu esse utilizati per inizià a sintesi di cDNA di u primu filu, è a specificità relativa di ogni metudu afecta a quantità è u tipu di cDNA sintetizatu.
U metudu di prima aleatoriu hè u menu specificu di i trè metudi.I primers sò annealed in parechji siti in tutta a trascrizione per pruduce cDNA di corta lunghezza parziale.Stu metudu hè spessu usatu per ottene sequenze terminali 5′ è cDNA da mudelli di RNA cù regioni strutturali secondarie o cù siti di terminazione chì a transcriptase inversa ùn pò micca riplicà.Per ottene u cDNA più longu, u rapportu di primers à RNA in ogni mostra di RNA deve esse determinatu empiricamente.A cuncentrazione iniziale di primers random varia da 50 à 250ng per 20μl di sistema di reazione.Perchè l'ADNc sintetizatu da l'RNA tutale utilizendu primers aleatoriu hè principalmente RNA ribosomi, poly (A) + RNA hè generalmente sceltu cum'è mudellu.
L'iniziu di l'Oligo (dT) hè più specificu di i primers random.Si hibridizza cù a coda poli(A) chì si trova à l'estremità 3' di mRNA in a maiò parte di e cellule eucariote.Perchè u poli(A) + RNA hè di circa 1% à 2% di l'RNA tutale, a quantità è a cumplessità di cDNA hè assai menu chè s'ellu era utilizatu primers aleatoriu.A causa di a so alta specificità, l'oligo (dT) generalmente ùn necessita micca ottimisazione per u ratio di RNA à primer è a selezzione di poly (A) +.Hè cunsigliatu di utilizà 0.5μg oligo (dT) per 20μl sistema di reazione.oligo (dT) 12-18 hè adattatu per a maiò parte di RT-PCR.U sistema ThermoScript RT-PCR furnisce oligo (dT) 20 per via di a so bona stabilità termica è hè adattatu per a temperatura di mantene più altu.
I primers specifichi di geni (GSP) sò i migliori primers specifichi per u passu di trascrizione inversa.GSP hè un oligonucleoside antisensu chì pò hibridà specificamente cù sequenze di destinazione di RNA, piuttostu cà anneal tutti Rnas cum'è primers aleatorii o oligo (dT).E regule utilizzate per cuncepisce i primeri PCR si applicanu ancu à u disignu di a reazione di trascrizione inversa GSP.GSP pò esse a listessa sequenza cum'è l'amorce di amplificazione annealed à a fine di mRNA3', o GSP pò esse designatu per esse annealed downstream cù l'amorce di amplificazione inversa.Per certi ogetti amplificati, hè necessariu di disignà più di un primer antisensu per una RT-PCR successu perchè a struttura secundaria di l'RNA di destinazione pò impedisce à u primer di ligà.Hè suggeritu di utilizà 1pmol GSP antisensu in u primu sistema di reazione di sintesi di a catena di 20μl.
2. Aumentà a temperatura di conservazione di u calore di a trascrizione inversa:
Per prufittà pienamente di a specificità GSP, deve esse aduprata a transcriptase inversa cù una stabilità termale alta.A transcriptase inversa stabile à u calore pò esse insulata à temperature più altu per aumentà u rigore di a reazione.Per esempiu, se un GSP hè annealed à 55 ° C, allora a specificità di GSP ùn hè micca utilizata cumplettamente se a trascrizione inversa hè realizata à 37 ° C cù pocu rigore cù AMV o M-MLV.In ogni casu, SuperScripⅡ è ThermoScript ponu reagisce à 50 ℃ o più altu, chì elimina i prudutti micca specifichi pruduciuti à temperature più bassu.Per a massima specificità, a mistura di RNA / primer pò esse trasferita direttamente da a temperatura di denaturazione di 65 ℃ à a temperatura di mantene a trascrizione inversa cù l'aghjunzione di una mistura di reazione 2x preriscaldata (iniziu termale di sintesi di cDNA).Questu aiuta à prevene l'accoppiamentu di basa trà e molécule à basse temperature.L'usu di un strumentu PCR simplificà e numerose transizioni di temperatura necessarie per a RT-PCR.
3. Reduce a contaminazione di DNA genomicu:
Una difficultà potenziale cù RT-PCR hè chì l'RNA contamina l'ADN genomicu.L'usu di metudi di separazione di RNA megliu, cum'è Trizol Reagent, riduce a contaminazione di DNA genomicu in preparazione di RNA.Per evitari i prudutti di l'ADN genomicu, l'RNA pò esse trattatu cù DnasⅠ di qualità di amplificazione per sguassà l'ADN contaminatu prima di a trascrizione inversa.I campioni sò stati mantenuti à 65 ℃ in 2.0mM EDTA per 10 min per finisce a digestione di DNaseⅠ.L'EDTA chelate l'ioni di magnesiu per prevene l'idrolisi di l'RNA dipendente di l'ioni di magnesiu chì si trova à alte temperature.
Per separà l'ADNc amplificatu da u pruduttu di l'amplificazione di l'ADN di u genoma, i primers chì anu anneal separatamente cù l'esone separatu ponu esse designati.I prudutti PCR derivati da cDNA seranu più brevi di quelli derivati da DNA genomicu contaminatu.Un esperimentu cuntrullatu senza trascrizzione inversa hè ancu realizatu nantu à ogni mudellu di RNA per determinà se un fragmentu determinatu hè da DNA genomicu o cDNA.I prudutti di PCR ottenuti in l'absenza di trascrizione inversa sò derivati da u genoma.
Prodottu Relativu
-U kit in un passu permette a trascrizione inversa è a PCR per esse realizatu in u stessu tubu.Hè solu bisognu di aghjunghje RNA template, primers PCR specifichi è ddH RNase-Free2O.
-L'analisi quantitativa in tempu reale di RNA pò esse realizatu rapidamente è precisamente.
-U kit usa un reattivu di trascrizione inversa Foregene unicu è Foregene HotStar Taq DNA Polymerase cumminatu cù un sistema di reazione unicu per migliurà efficacemente l'efficienza di amplificazione è a specificità di a reazione.
-U sistema di reazione ottimisatu face chì a reazione hà una sensibilità di rilevazione più alta, una stabilità termica più forte è una tolleranza megliu.
-Capacità efficace per sguassà gDNA, chì pò sguassà gDNA in u mudellu in 2 minuti.
-Efficace sistema di trascrizione inversa, ci vole solu 15 minuti per compie a sintesi di u primu filu cDNA.
-Modelli cumplessi: mudelli cù un altu cuntenutu di GC è una struttura secundaria cumplessa pò ancu esse invertitu cù alta efficienza.
-Sistema di trascrizione inversa di alta sensibilità, mudelli pg-level ponu ancu ottene cDNA di alta qualità.
-U sistema di trascrizione inversa hà una alta stabilità termica, a temperatura ottimale di reazione hè 42 ℃, è hà sempre una bona prestazione di trascrizione inversa à 50 ℃.
Tempu di Postu: Mar-07-2023